Metagenómica Barcoding
Estudiamos la composición del perfil de la comunidad bacteriana y arquea (16S) o eucariota (18S/ITS)
Servicio especializado
Análisis del perfil taxonómico y diversidad de la microbiota
El objetivo es el análisis del perfil taxonómico y diversidad de las bacterias, arqueas u hongos presentes en una muestra.
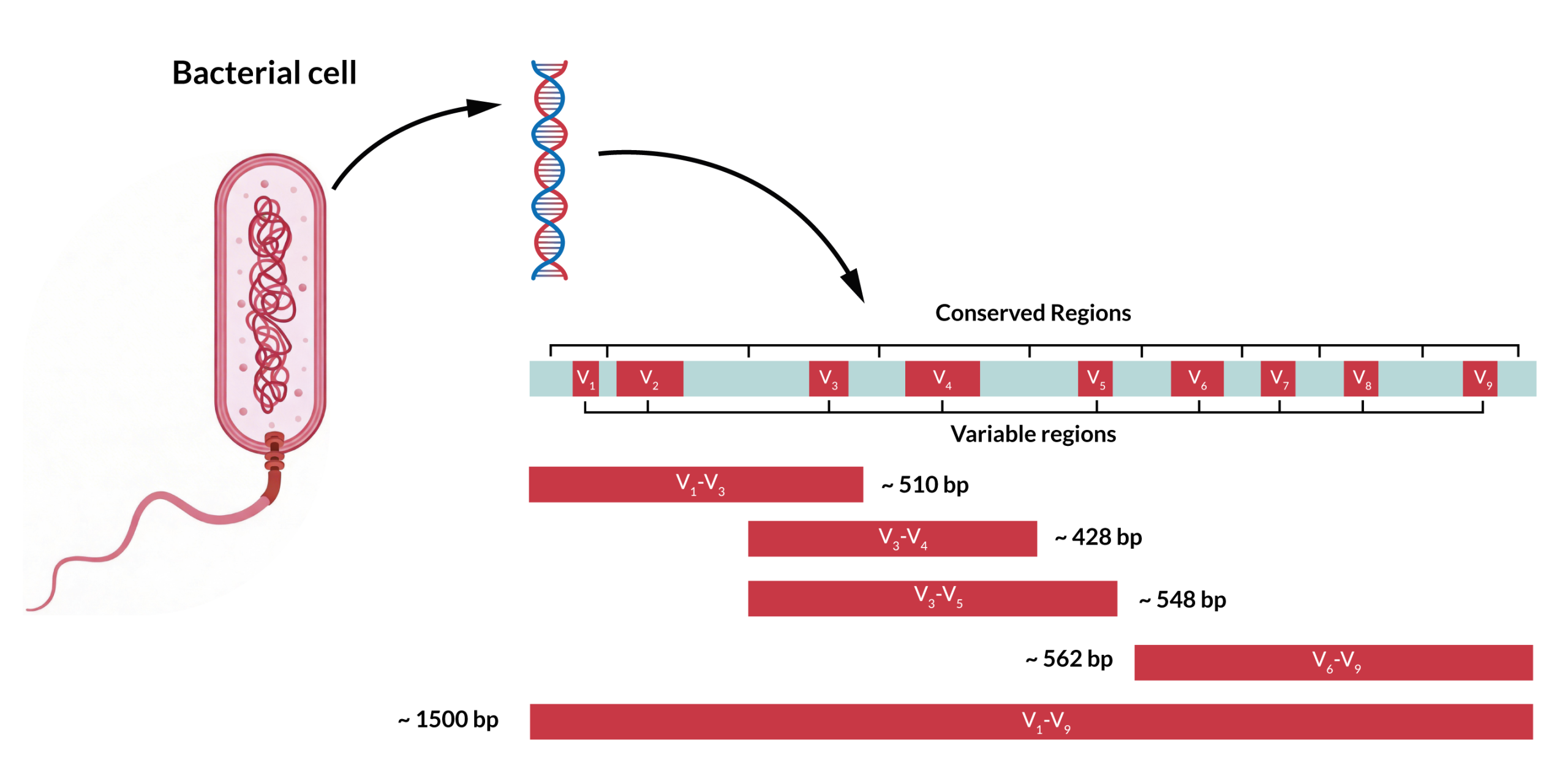
El 16S rRNA es un gen exclusivo de organismos procariotas, mitocondrias y cloroplastos, con una secuencia nucleotídica altamente conservada que intercala nueve regiones hipervariables, siendo las V3-V4 las más estudiadas. Estas regiones son secuencias distintivas para cada grupo filogenético actuando como marcadores. Mediante su amplificación y secuenciación se determinará la composición de la microbiota de la muestra comparando con bases de datos de referencia.
En el caso de hongos, al ser eucariotas, las regiones utilizadas para el metabarcoding suelen ser el gen 18S rRNA y el espaciador ITS bajo el mismo principio; secuencias únicas para cada grupo filogenético. El Espaciador Transcrito Interno (ITS, por sus siglas en inglés) son dos secuencias de ADN no codificante situado entre los genes de las subunidades del ribosoma de la mayoría de las especies eucariotas.
La elección del marcador a amplificar en estudios de barcoding dependerá de la fracción del metagenoma que se pretenda estudiar, así como del tipo de muestra, pues unas regiones serán más adecuadas que otras para anotar ciertos taxones. Esta decisión se deberá abordar en la fase del diseño del estudio.
¿Qué incluye nuestro servicio?
Asesoramiento científico técnico
- Diseño experimental
- Estrategia de análisis
- Protocolo de muestreo
- Soluciones de logística de las muestras
- Servicio de biobanco y almacenamiento hasta su análisis
Extracción de ADN, preparación de librerías y secuenciación
- Laboratorio con sala blanca certificada
- Uso de controles positivos y negativos
- Selección de marcadores específicos y protocolos de purificación según matriz
Análisis bioinformático personalizado
- Filtrado de calidad y validación con histórico de análisis
- Diversidad alfa y beta, perfiles taxonómicos basados en ASVs
- Inferencia funcional procariota y estadística con modelos especializados y pipelines propias validadas
- 2 horas de análisis post-entrega en cualquier estudio completo
Reunión de entrega de resultados.
- Informes interactivos con gráficos y tablas dinámicas. Contenido de material y métodos
- Figuras descargables preparados para publicar
Más información
Consulta las fichas técnicas de servicio.
Preguntas Frecuentes sobre nuestro Servicio de Metagénomica Barcoding
¿En qué tipos de estudios se aplica la técnica de metabarcoding?
El metabarcoding 16S para procariotas (y 18S/ITS para eucariotas/hongos) se aplica en análisis de microbiota para múltiples sectores:
- Salud: microbioma intestinal, oral, piel o vaginal
- Agricultura: suelo, rizosfera o biocontrol
- Ambiental: agua, aire, biorremediación
- Veterinaria, producción animal y alimentación (seguridad e higiene)
Permite conocer la comunidad de microorganismos presente en una muestra y hacer comparaciones entre lotes, tratamientos, tiempos, manejos… ideal para proyectos de investigación y control de calidad industrial. El tipo de diseño y seguimiento dependerá de los objetivos, trabajando en estudios observacionales, tratado-control, longitudinales o de intervención.
¿Qué muestras se pueden analizar?
Trabajamos con una amplia variedad de matrices, con protocolos de extracción y purificación en más de 50 diferentes, incluyendo algunas de muy baja biomasa. Cada una tiene sus particularidades como contaminantes o inhibidores, que deberán abordarse de forma específica para conseguir una buena calidad de ADN para la construcción de librerías.
Algunos ejemplos de matrices son: Muestras humanas (heces, saliva, hisopos naso/orofaríngeos, piel/mucosas, strips), veterinarias (heces, biopsias, hisopos, orina), ambientales y agrícolas (suelo, rizosfera/raíces, agua dulce/marina filtrada, sedimentos, aire filtrado), superficies/biofilms e ingredientes y alimentos.
Las muestras biológicas deberán muestrearse, transportarse y almacenarse teniendo en cuenta los análisis posteriores a los que serán sometidas. Existen diferentes opciones para el muestreo como el uso de bacteriostáticos, usados para reducir los sesgos de muestreo.
También ofrecemos el servicio de optimización en nuevas matrices.
¿Qué información se obtiene con el análisis de microbiota por metabarcoding?
El metabarcoding 16S (y 18S/ITS para eucariotas/hongos) ofrece un perfil taxonómico de la comunidad microbiana con abundancias relativas por muestra y grupo.
Incluye diversidad alfa/beta, comparativas entre condiciones y taxones diferenciales como posibles biomarcadores. La resolución suele ser a género (especie cuando la región/DB lo permite: SILVA/UNITE), con límites de detección dependientes de la matriz y la profundidad.
¿Cómo recibiré los resultados?
Durante todo el proceso contarás con la asistencia de un Project Manager que te informará del estado de tu proyecto. Una vez finalizado el análisis, recibirás un archivo pdf con una guía y las credenciales para la descarga de los resultados desde el servidor de Microomics. Obtendrás los datos de secuenciación en bruto, un informe con el material y métodos del proyecto y un formato .html donde podrás navegar por los resultados mediante tablas y gráficos dinámicos, descargarte figuras y realizar comparativas entre modelos de comparación.
¿Cuánto tiempo tarda el análisis?
El tiempo de realización de cada proyecto varía considerablemente dependiendo del número de etapas que Microomics realice (extracción, preparación de librerías, secuenciación, bioinformática) así como del tipo de muestras analizadas y número de muestras. Para estudios de metabarcoding, los tiempos de entrega puede variar entre 4 y 12 semanas. Recomendamos contactar con nuestro equipo para obtener una aproximación más precisa.
¿Cuál es la diferencia entre metagenómica barcoding y metagenómica shotgun?
La metagenómica por barcoding (metabarcoding 16S/18S/ITS) amplifica por PCR un gen marcador y genera perfiles taxonómicos con abundancias relativas; es más rápida y económica, pero con menor resolución (generalmente a género).
La metagenómica shotgun secuencia todo el ADN de la muestra (sin PCR dirigida), permitiendo identificación a especie/cepa, análisis funcional (genes) y recuperación de MAGs; requiere mayor profundidad, presupuesto y procesamiento bioinformático.
A modo de resumen; metabarcoding para caracterización comparativa eficiente del microbioma centrada en taxonomía; shotgun cuando se necesita máxima resolución y funciones. Recomendamos contactar con el equipo de Microomics y plantear los objetivos del proyecto para poder decidir sobre el tipo de aproximación al estudio del microbioma más adecuada.
Formulario de Contacto
Contacta con Nosotros
Dirección
C/ Laureà Miró, 405-410
08980, Sant Feliu del Llobregat
Barcelona
Contacto
info@microomics.com
Tel: +34 938 874 488
Horario
Viernes: 9:00 – 15:00