Metagenómica shotgun
Análisis del perfil taxonómico, funcional y diversidad de las bacterias, y análisis del perfil taxonómico y diversidad de hongos y/o virus
Servicio especializado
Análisis del perfil taxonómico, funcional y diversidad
La metagenómica shotgun permite conocer la composición y función de comunidades microbianas presentes en cualquier tipo de muestra sin necesidad de cultivo previo (heces, saliva, suelo, agua y otras).
A diferencia de las técnicas de mertabarcoding dirigidas como la secuenciación del gen 16S rRNA, el estudio del microbioma mediante shotgun genera una fragmentación y secuenciación completa del ADN de la muestra. Esto permite:
- Identificación taxonómica de alta resolución, llegando hasta nivel de especie o cepa.
- Caracterización funcional completa del microbioma anotando genes y sus funciones.
- Detección de elementos móviles y genes de resistencia antibiótica o relacionados con alguna característica en concreto de los taxones.
Requiere de un control metodológico exhaustivo en la parte de laboratorio y en la de análisis bioinformático, pudiendo integrar la información del microbioma con otras variables recogidas durante el experimento.
Este análisis metagenómico completo es ideal para investigaciones que requieren no solo saber «quién está ahí» sino también «qué pueden hacer» los microorganismos, siendo fundamental en áreas como el desarrollo de biomarcadores microbianos, el estudio de resistomas y la monitorización de intervenciones terapéuticas.
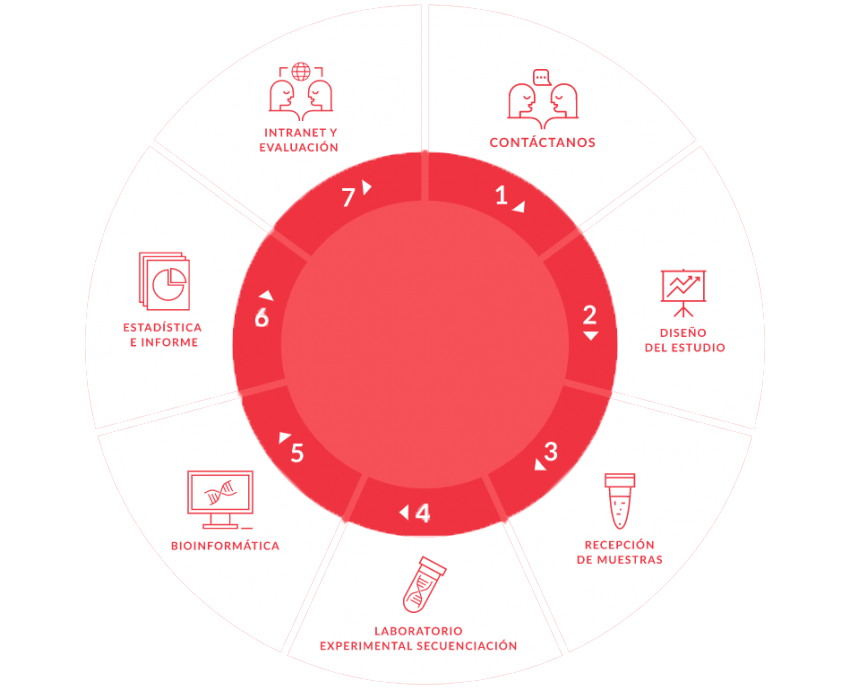
¿Qué incluye nuestro servicio?
Asesoramiento científico-técnico
- Diseño experimental
- Estrategia de análisis
- Protocolo de muestreo
- Soluciones de logística de las muestras
- Servicio de biobanco y almacenamiento hasta su análisis
Extracción de ADN y secuenciación
- Laboratorio con sala blanca certificada
- Protocolos de extracción y purificación validados para más de 50 matrices
- Medida de calidad de la librería mediante electroforesis capilar
- Illumina NovaSeq 2×150 pb
- 40 millones de lecturas (20M paired-end) garantizados por muestra, ajustables
Análisis bioinformático personalizado
- Filtrado de calidad y validación con histórico de proyectos de la empresa
- Pipelines propias diseñadas para personalizar cada análisis
- Asignación taxonómica, análisis de diversidad taxonómica y anotación funcional. Complementos de ensamblaje de novo, MAGs y análisis de enriquecimiento de rutas metabólicas
- 2 horas de análisis post-entrega en cualquier estudio completo
Reunión de entrega de resultados
- Informes interactivos con gráficos y tablas dinámicas
- Contenido de material y métodos
- Figuras descargables preparados para publicar en la vanguardia de la técnica
Más información
Consulta las fichas técnicas de servicio.
Preguntas Frecuentes sobre nuestro Servicio de Metagénomica Shotgun
¿Qué es la metagenómica shotgun y cuándo conviene usarla?
La metagenómica shotgun es secuenciación metagenómica del ADN total de la muestra (sin PCR dirigida). Permite un perfil taxonómico y funcional con resolución a especie/cepa, detección de genes/enzimas y rutas, resistoma y virulencia. Es la opción recomendada cuando necesitas máxima resolución, estudiar funciones metabólicas o recuperar MAGs (genomas ensamblados a partir de metagenomas).
¿Qué muestras se pueden analizar?
Nuestro servicio de análisis metagenómico shotgun es versátil y compatible con todo tipo de muestras:
- Humanas: microbioma intestinal, oral, piel o vaginal.
- Ambientales: microbioma de suelo, agua (marino, dulce), aire.
- Agroalimentarias: microbioma vegetal (endófitos, epífitos), alimentos fermentados, suelos, superficies industriales.
- Animales: microbioma de rumiantes, aves o peces.
Procesamos más de 50 matrices con protocolos validados, asegurando alta calidad en la extracción de ADN y secuenciación shotgun. No dudes en consultarnos sobre el tipo de muestras de tu estudio.
¿En qué tipos de estudios se aplica la metagenómica shotgun?
Cuando se requiere dar respuesta a las dos preguntas “¿qué microorganismos están presentes en esta muestra a nivel de especie?” y “¿qué capacidad metabólica tienen los microorganismos presentes en esta muestra?” Pudiendo identificar biomarcadores funcionales con valor pronóstico o diágnostico en estudios de evaluación de producto, manejo comparativo de grupos control-tratado, estudios longitudinales de caracterización, estudios descriptivos y otros diseños.
¿Qué profundidad de secuenciación recomendáis?
Depende de la complejidad de la matriz y los objetivos: desde 5–10 millones de lecturas por muestra (perfil taxonómico/funcional básico) hasta 20–50+ millones para MAGs o detección fina de genes escasos. Recomendamos que nos escribáis a través del formulario de contacto para poder valorar el proyecto en conjunto.
¿Cómo recibiré los resultados?
Durante todo el proceso contarás con la asistencia de un Project Manager que te informará del estado de tu proyecto. Una vez finalizado el análisis, recibirás un archivo pdf con una guía y las credenciales para la descarga de los resultados desde el servidor de Microomics. Obtendrás los datos de secuenciación en bruto, un informe con el material y métodos del proyecto y un archivo .html donde podrás navegar por los resultados mediante tablas y gráficos dinámicos, descargarte figuras y realizar comparativas entre modelos de alfa y beta diversidad.
¿Cómo garantizáis la calidad de los datos y entregables?
Microomics cuenta con una sala blanca certificada propia para realizar las extracciones de ADN. Además, trabajamos con controles negativos (blancos de extracción/NTC) y positivos (mock community), generando puntos de control donde evaluamos el desarrollo del proyecto. Durante todo el proceso, estamos en contacto con el investigador informando sobre el avance de sus muestras por nuestro circuito.
¿Cuál es la diferencia entre metagenómica barcoding y metagenómica shotgun?
La metagenómica por barcoding (metabarcoding 16S/18S/ITS) amplifica por PCR un gen marcador y genera perfiles taxonómicos con abundancias relativas; es más rápida y económica, pero con menor resolución (generalmente a género).
La metagenómica shotgun secuencia todo el ADN de la muestra (sin PCR dirigida), permitiendo identificación a especie/cepa, análisis funcional directo (genes/vías) y recuperación de MAGs; requiere mayor profundidad, presupuesto y procesamiento bioinformático.
A modo de resumen; metabarcoding para caracterización comparativa eficiente del microbioma; shotgun cuando se necesita máxima resolución y funciones. Recomendamos contactar con el equipo de Microomics y plantear los objetivos del proyecto para poder decidir sobre el tipo de aproximación al estudio del microbioma más adecuada.
Formulario de Contacto
Contacta con Nosotros
Dirección
C/ Laureà Miró, 405-410
08980, Sant Feliu del Llobregat
Barcelona
Contacto
info@microomics.com
Tel: +34 938 874 488
Horario
Viernes: 9:00 – 15:00



